Search Nipponbare
| Mutant Information |
|---|
| Mutant Name | FN2629-S [Download] |
| Generation | M2 |
| Genus Species | Oryza Sativa |
| Cultivar | Kitaake |
| Alignment File (BAM File) | Download FN2629-S Alignment File |
| Seed Availability | Yes [Order Seeds] |
| Mapping (Hover to Zoom-In) | 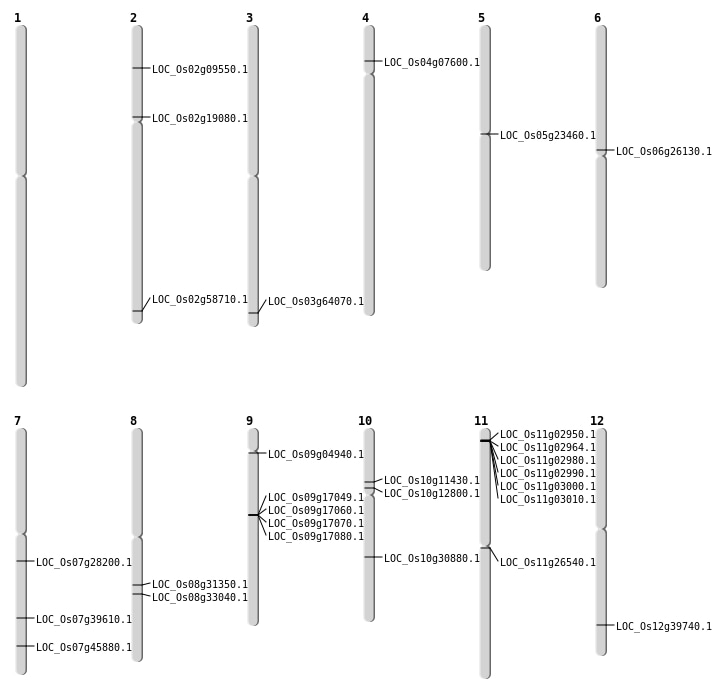
|
| Variant Information |
|---|
Single base substitutions: 83
| Variant Type | Chromosome | Position | Change | Genotype | Effect | Gene Affected |
|---|---|---|---|---|---|---|
| SBS | Chr1 | 15189797 | T-G | HET | ||
| SBS | Chr1 | 15621290 | G-T | HET | ||
| SBS | Chr1 | 16881365 | T-C | HET | ||
| SBS | Chr1 | 16995427 | T-C | HET | ||
| SBS | Chr1 | 2255333 | C-T | HET | ||
| SBS | Chr1 | 25146124 | G-A | HET | ||
| SBS | Chr1 | 31540518 | C-G | HET | ||
| SBS | Chr1 | 34823932 | C-G | HET | ||
| SBS | Chr1 | 36559634 | G-A | HET | ||
| SBS | Chr1 | 36699540 | G-A | HET | ||
| SBS | Chr1 | 40790404 | C-A | HET | ||
| SBS | Chr1 | 41326526 | G-T | HET | ||
| SBS | Chr10 | 10264155 | G-A | HET | ||
| SBS | Chr10 | 1053176 | C-T | HET | ||
| SBS | Chr10 | 12041952 | T-C | HET | ||
| SBS | Chr10 | 5848005 | C-T | HET | ||
| SBS | Chr10 | 614036 | A-G | HET | ||
| SBS | Chr10 | 6331050 | G-C | HET | NON_SYNONYMOUS_CODING | LOC_Os10g11430 |
| SBS | Chr10 | 7147079 | G-T | HET | NON_SYNONYMOUS_CODING | LOC_Os10g12800 |
| SBS | Chr10 | 7792754 | C-T | HET | ||
| SBS | Chr11 | 11153742 | C-T | HET | ||
| SBS | Chr11 | 1152675 | G-T | HET | ||
| SBS | Chr11 | 15211820 | G-T | HET | NON_SYNONYMOUS_CODING | LOC_Os11g26540 |
| SBS | Chr11 | 15428551 | A-G | HET | ||
| SBS | Chr11 | 17537958 | G-T | HET | ||
| SBS | Chr11 | 17683564 | C-T | HET | ||
| SBS | Chr11 | 21659229 | G-A | HET | ||
| SBS | Chr11 | 2686224 | C-A | HET | ||
| SBS | Chr12 | 18167773 | G-A | HET | ||
| SBS | Chr12 | 21911129 | G-T | HET | ||
| SBS | Chr2 | 11137693 | C-T | HET | NON_SYNONYMOUS_CODING | LOC_Os02g19080 |
| SBS | Chr2 | 11634661 | G-A | HET | ||
| SBS | Chr2 | 13872971 | G-T | HET | ||
| SBS | Chr2 | 18853268 | T-C | HET | ||
| SBS | Chr2 | 21966118 | T-A | HET | ||
| SBS | Chr2 | 21966119 | C-T | HET | ||
| SBS | Chr2 | 2477547 | C-T | HET | ||
| SBS | Chr2 | 31701825 | C-T | HET | ||
| SBS | Chr2 | 35073305 | C-A | HET | ||
| SBS | Chr2 | 4918815 | C-T | HET | NON_SYNONYMOUS_CODING | LOC_Os02g09550 |
| SBS | Chr3 | 16394444 | C-T | HET | ||
| SBS | Chr3 | 36204771 | A-G | HET | NON_SYNONYMOUS_CODING | LOC_Os03g64070 |
| SBS | Chr3 | 6182949 | C-A | HET | ||
| SBS | Chr4 | 10179950 | C-T | HET | ||
| SBS | Chr4 | 11592522 | A-T | HET | ||
| SBS | Chr4 | 14632538 | A-T | HET | ||
| SBS | Chr4 | 1680115 | G-A | HET | ||
| SBS | Chr4 | 19302856 | G-T | HET | ||
| SBS | Chr4 | 30662169 | G-A | HET | ||
| SBS | Chr4 | 4040151 | G-A | HET | NON_SYNONYMOUS_CODING | LOC_Os04g07600 |
| SBS | Chr5 | 14544369 | T-A | HET | ||
| SBS | Chr5 | 16856243 | G-A | HET | ||
| SBS | Chr5 | 19977283 | T-C | HET | ||
| SBS | Chr5 | 996350 | T-G | Homo | ||
| SBS | Chr5 | 9986904 | C-A | HET | ||
| SBS | Chr6 | 11042753 | C-T | HET | ||
| SBS | Chr6 | 14303931 | G-A | HET | ||
| SBS | Chr6 | 14707954 | G-A | HET | ||
| SBS | Chr6 | 15290963 | C-T | HET | NON_SYNONYMOUS_CODING | LOC_Os06g26130 |
| SBS | Chr6 | 17263254 | G-A | HET | ||
| SBS | Chr6 | 20444498 | T-C | HET | ||
| SBS | Chr7 | 16465124 | G-A | HET | NON_SYNONYMOUS_CODING | LOC_Os07g28200 |
| SBS | Chr7 | 17397754 | G-A | HET | ||
| SBS | Chr7 | 18427437 | A-G | HET | ||
| SBS | Chr7 | 21943120 | G-A | HET | ||
| SBS | Chr7 | 22833173 | A-G | HET | ||
| SBS | Chr7 | 23739514 | G-C | HET | NON_SYNONYMOUS_CODING | LOC_Os07g39610 |
| SBS | Chr7 | 26035604 | C-T | HET | ||
| SBS | Chr7 | 27377081 | C-T | HET | NON_SYNONYMOUS_CODING | LOC_Os07g45880 |
| SBS | Chr7 | 28085146 | G-T | HET | ||
| SBS | Chr7 | 28770681 | T-C | HET | ||
| SBS | Chr7 | 6516504 | G-T | HET | ||
| SBS | Chr7 | 6579764 | C-T | HET | ||
| SBS | Chr7 | 8425135 | T-C | HET | ||
| SBS | Chr7 | 8924239 | G-A | HET | ||
| SBS | Chr7 | 9704315 | A-G | HET | ||
| SBS | Chr8 | 12075743 | G-T | HET | ||
| SBS | Chr8 | 14342046 | C-T | HET | ||
| SBS | Chr8 | 19389863 | G-A | HET | NON_SYNONYMOUS_CODING | LOC_Os08g31350 |
| SBS | Chr8 | 20513852 | G-A | HET | NON_SYNONYMOUS_CODING | LOC_Os08g33040 |
| SBS | Chr8 | 24446959 | G-A | HET | ||
| SBS | Chr9 | 2653844 | G-A | HET | NON_SYNONYMOUS_CODING | LOC_Os09g04940 |
| SBS | Chr9 | 8233030 | C-A | HET |
Deletions: 18
| Variant Type | Chromosome | Start | End | Size (bp) | Number of Genes |
|---|---|---|---|---|---|
| Deletion | Chr5 | 194174 | 194178 | 4 | |
| Deletion | Chr5 | 786658 | 786665 | 7 | |
| Deletion | Chr12 | 954150 | 954154 | 4 | |
| Deletion | Chr11 | 1018001 | 1047000 | 28999 | 6 |
| Deletion | Chr5 | 1104674 | 1104686 | 12 | |
| Deletion | Chr8 | 1381380 | 1381383 | 3 | |
| Deletion | Chr11 | 1640790 | 1640792 | 2 | |
| Deletion | Chr2 | 2942935 | 2942937 | 2 | |
| Deletion | Chr12 | 8572081 | 8572091 | 10 | |
| Deletion | Chr9 | 10451001 | 10473000 | 21999 | 4 |
| Deletion | Chr7 | 12260562 | 12260563 | 1 | |
| Deletion | Chr5 | 13414324 | 13414346 | 22 | LOC_Os05g23460 |
| Deletion | Chr1 | 19132162 | 19132168 | 6 | |
| Deletion | Chr10 | 20726301 | 20726315 | 14 | |
| Deletion | Chr3 | 21808409 | 21808413 | 4 | |
| Deletion | Chr12 | 24545226 | 24545240 | 14 | LOC_Os12g39740 |
| Deletion | Chr8 | 27446685 | 27446691 | 6 | |
| Deletion | Chr2 | 35871335 | 35871336 | 1 | LOC_Os02g58710 |
Insertions: 5
| Variant Type | Chromosome | Start | End | Size (bp) | Number of Genes |
|---|---|---|---|---|---|
| Insertion | Chr10 | 16106548 | 16106550 | 3 | LOC_Os10g30880 |
| Insertion | Chr2 | 34251808 | 34251810 | 3 | |
| Insertion | Chr3 | 4898410 | 4898411 | 2 | |
| Insertion | Chr5 | 24413003 | 24413004 | 2 | |
| Insertion | Chr9 | 4919476 | 4919476 | 1 |
No Inversion
Translocations: 4
| Variant Type | Chromosome | Position 1 | Chromosome | Position 2 | Number of Genes |
|---|---|---|---|---|---|
| Translocation | Chr4 | 654145 | Chr2 | 5658572 | |
| Translocation | Chr11 | 1589518 | Chr2 | 9833429 | |
| Translocation | Chr11 | 23663019 | Chr6 | 11605812 | |
| Translocation | Chr11 | 24207834 | Chr10 | 11150143 |
